跟进我的 上一篇关于全基因组 CRISPR 文库的文章,我认为多展示一点会很有用。
在做图书馆工作时有很多事情要考虑,但有两个主要的
- 您有多确定命中源于目标活动与 不中 诡计?
- 图书馆的哪一部分是功能性的?
开与关目标是真正令人担忧的问题,因为您可能会花费大量时间来追踪虚假命中。 CRISPR (和 sh/siRNA)文库以冗余方式解决了这个问题,人们应该总是要求一个表型丰富对应于相同的多个指南 基因. 但是在冗余度相对较低的文库中(例如 GeCKOv1 每个基因只有 3-4 个指南),很容易被一个炙手可热的表型但只有一个指南的命中迷住。
对库功能部分的关注更具技术性,但会影响屏幕的易用性和上方的冗余点。 如果您的许多指南都不起作用,那么与较小的库相比,克隆和转换大型库的所有额外工作都是白费力气。 更糟糕的是,每个非功能性指南都会减少您冗余的机会。
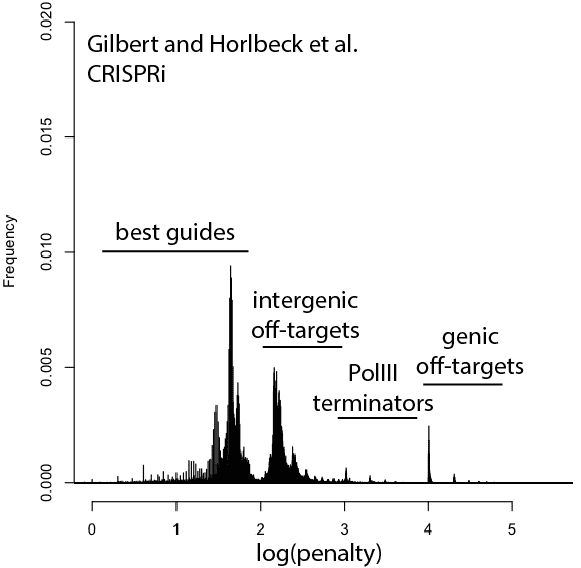
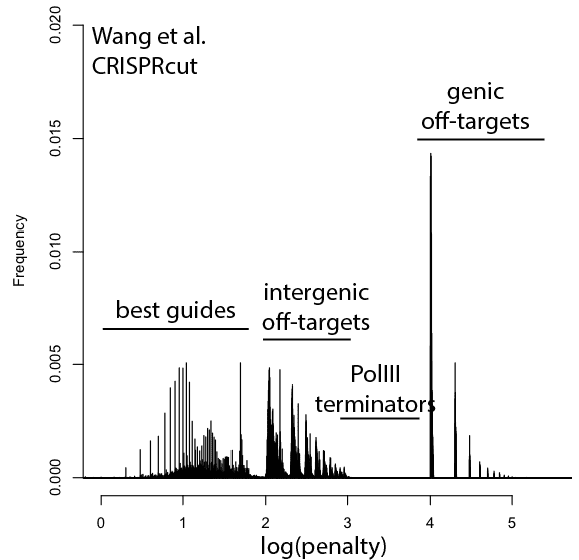
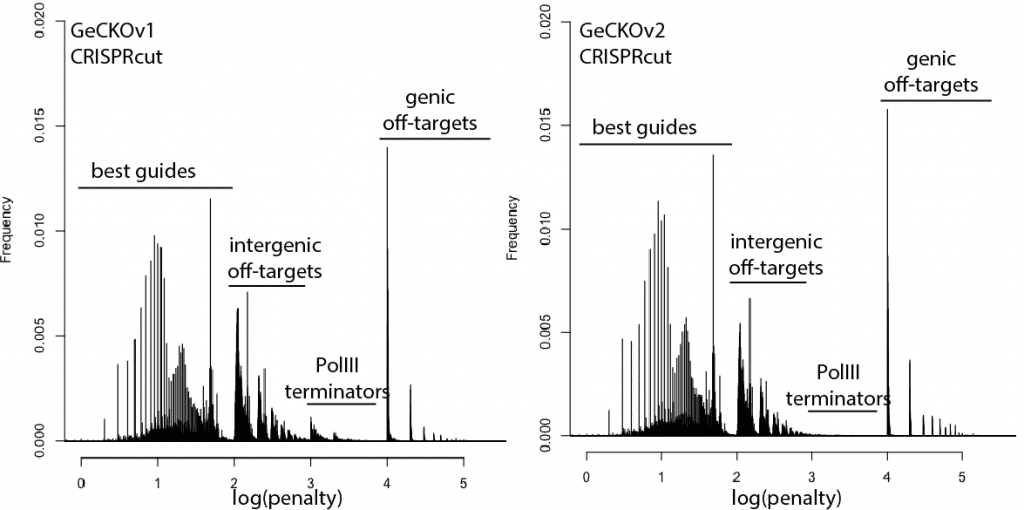
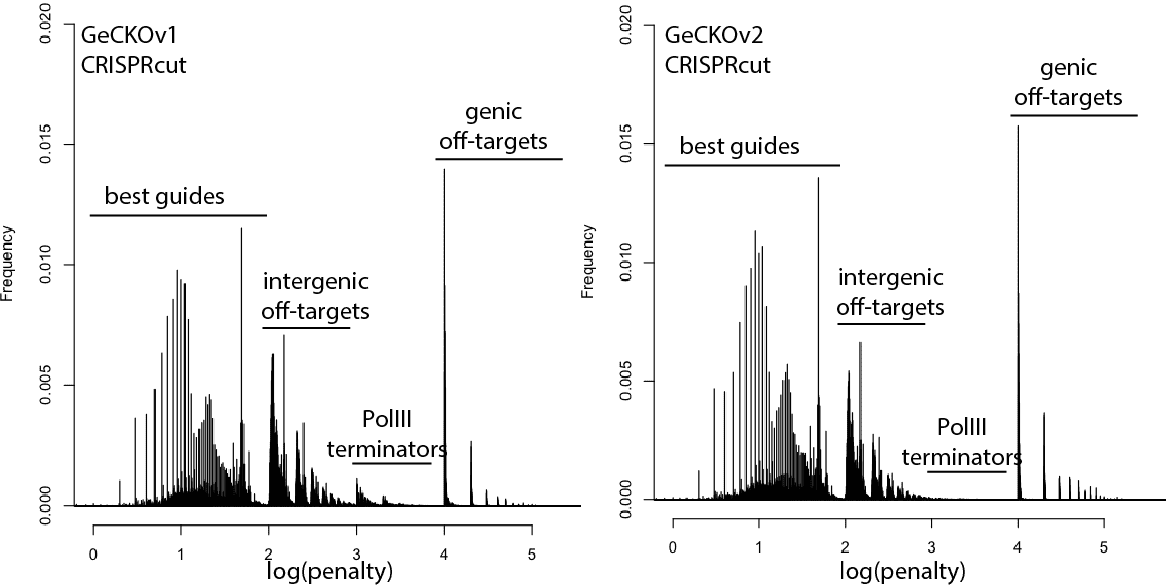
考虑到这一点,这里是现有的更新发行版 基因组- 针对人类的广泛指南库 细胞. “惩罚”轴采用对数刻度,惩罚很容易解释以突出问题的类别。 对于惩罚,十位代表指南本身的分数,100 位代表基因间脱靶的数量,1000 位代表基因脱靶。
例如,log(penalty)=0-2 的任何东西都没有脱靶并且可能没问题,尽管随着接近 2.log(penalty)=2-3 的指南有更高的机会完全失效脱靶,每 100 次冲击额外的脱靶命中(例如,100 = 200 次脱靶,3 = 4 次脱靶等)。 log(penalty)=XNUMX-XNUMX 包含 Pol III 终止子序列并且可能永远不会 转录. log(penalty)=4+ 有 基因的 脱靶,每 100-spike 一个额外的脱靶影响基因(例如,惩罚 1000 = 一个脱靶,2000 = 两个脱靶)。 这些惩罚是复合的,所以 2,354 的分数意味着两个基因脱靶、3 个基因间脱靶和 54 的指导惩罚。
请注意,调用 genic 与 intergenic 是使用 集合数据 并且对 CRISPR 实验的类型很敏感。 克里斯普里 寻找基因的 -50 到 +300 内的命中,而 CRISPRcutting 则着眼于外显子(目前我们将撇开在潜在功能性内含子或 UTR 区域内切割的可怕前景)。
总的来说,CRISPRi 的情况看起来不错。 这里有一点优势,因为 CRISPRi 似乎只在转录起始位点周围的狭窄窗口中起作用,因此脱靶点不太可能击中基因。 CRISPRcutting 文库在注释外显子中的脱靶方面做得并不好,只有更深入的每个指南分析才能判断指南冗余是否会处理错误调用的表型。 很高兴看到 GeCKO 在 v2 中得到了改进(例如摆脱了终止子序列),希望 v3 可以控制一些基因脱靶。
我想强调的是,所有这些库都运行良好,并已成功用于提供生物学洞察力。 但是在使用每个库并考虑使用它们时产生的点击量时,请记住这些指南属性。