
Hani Goodarzi es profesor asistente en el Departamento de Biofísica y Bioquímica de la Universidad de California en San Francisco. En abril, comenzó a trabajar en un proyecto de investigación para descubrir el moléculas de ARN estructura del SARS-CoV-2 genoma,. En noviembre, habló con la escritora científica de IGI, Hope Henderson, sobre este proyecto.
Cuéntame un poco sobre tu proyecto COVID.
Como probablemente sepa, la información genética está codificada en las moléculas A, G, C y T para ADN. Para el ARN, es A, G, C y U. SARS-CoV-2, el virus que causa COVID-19, usa ARN en lugar de ADN para su código genético. En otras palabras, la molécula de ARN es lo que se transmite.
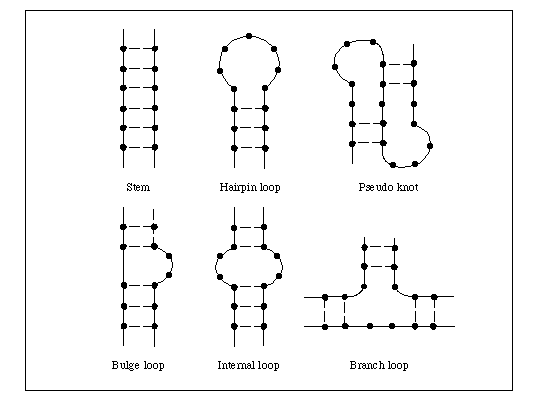
El ADN es una molécula de buen aspecto, ¿verdad? Es una doble hélice y la forma es estable. Pero el ARN es solo un hebra sencilla.. Para el ARN, existe un nivel de información genética de orden superior además de la secuencia de letras, que es la forma en que esta única hebra de ARN se pliega sobre sí misma. A esto se le llama estructura secundaria. Mi equipo está analizando la estructura secundaria del genoma del SARS-CoV-2.
¿Cómo se interesó por la estructura secundaria del ARN?

Cuando era un postdoctorado, comencé a trabajar en un proyecto con charlie arrozel laboratorio, tratando de comprender si hay información sobre cuándo los genes están activados o desactivados u otra información funcional en la estructura del ARN del ARN virus. Y de hecho, una de las familias de virus que analizamos fueron los coronavirus. Entonces, cuando sucedió el COVID-19, ya tenía una idea de la importancia del tipo de estructura del ARN en el ciclo de vida de este virus.
¿Cómo ves la estructura secundaria?
El proyecto en el que estamos trabajando ahora es básicamente tomar el genoma viral, cortarlo y observar las estructuras secundarias del ARN pieza por pieza con una resolución realmente alta. Estamos aprovechando una protocolo que fue desarrollado por Jonathan Weissmannlaboratorio aquí en UCSF, y le hemos hecho algunas modificaciones. Y eso nos ayuda a decodificar la estructura secundaria del genoma del ARN.
¿Qué haces después de cortar el ARN?
El método se llama DMS-MaPseq. La idea es que agregue una sustancia química, DMS, que puede modificar el ARN. Entonces, ¿cuánto cada ARN nucleótido - lo que llamamos un individuo A, C, G o U - se modifica depende de cuán expuesto esté ese nucleótido. Por ejemplo, si el ARN está plegado sobre sí mismo o forma una especie de doble hélice, la sustancia química ya no podrá acceder a él y no verá ninguna modificación. Si está en, digamos, un bucle o un bulto donde está abierto, obtendrá una modificación.
Además de esta reacción química, agrega una metodología de secuenciación de alto rendimiento que lee estas modificaciones como mutaciones en la secuencia. Cuantas más mutaciones vea después de agregar esta sustancia química, más modificación hubo y más expuesto estuvo ese nucleótido. Puede combinar los datos en los que se mutaron los nucleótidos con la secuencia de ARN y hacer predicciones sobre la estructura secundaria del ARN.
¿Comprender la estructura viral del SARS CoV-2 y el significado de esa estructura tendrá implicaciones en el tratamiento del COVID-19?
Si. Cuando hablamos de que el ARN viral es funcional, significa que juega un papel en el ciclo de vida del virus. Y hay un par de formas en las que puede apuntarlos terapéuticamente. Uno es apuntar a la propia estructura del ARN. Es inusual, pero hay algunas compañías farmacéuticas que están realmente enfocadas en apuntar al ARN mismo y detener la (SCD por sus siglas en inglés), de usar el ARN para hacer proteínas.
Otra forma en que se puede utilizar el conocimiento de la estructura para crear dianas terapéuticas se basa en el hecho de que las estructuras de ARN pueden ser un centro de interacción, donde actúan otros factores cruciales. Tienes proteínas de unión al ARN que interactúan con él. Tienes helicasa enzimas CRISPR-Cas que abren el ARN.
Entonces, si descubre la red de proteínas que interactúan con el genoma viral, también puede apuntar e interrumpir esas interacciones. Por ejemplo, si se necesita una helicasa para abrir la estructura del ARN para la replicación del virus, la inhibición de esa helicasa debería reducir la replicación viral.
¿Dónde estás en el proyecto?
El primer paso del proyecto fue básicamente cortar el genoma y luego clonar las piezas individuales en bacterias fotosintéticas que usamos como fábricas para hacer más copias de la pieza del genoma. Entonces ahí es donde estamos. Estamos solucionando problemas de esta parte. A continuación, es fundamental comprender cómo actúa realmente el ARN en una célula humana. Así que queremos poner los fragmentos de ARN en células humanas y luego usar la técnica DMS-MaPseq que mencioné.
¿Son estos trozos de ARN más cortos y “cortados” una representación precisa de cómo el ARN forma una estructura secundaria cuando está en una sola pieza?
Hay algunos trabajos que ya han resuelto la estructura secundaria del ARN del SARS-CoV-2, pero con menor resolución de la que pretendemos hacer. Pero eso significa que tenemos cierta información sobre las interacciones de mayor alcance con las que podemos trabajar. Probablemente perdamos algunas cosas al usar fragmentos, pero esto nos permitirá hacer esto con una resolución más alta. Así que es un escenario de pros y contras.
¿Tienes nuevos pasatiempos relacionados con la cuarentena?
Compramos una granja hidropónica de interior y comenzamos a cultivar hierbas.
¿Cómo van tus lechugas?
¡Son grandiosos! También lo son los tomates cherry y las hierbas. ¡Muy recomendable!
Este trabajo está financiado por el Laboratorio de Genómica Research (LGR), una colaboración entre UC Berkeley / UCSF (IGI) y GlaxoSmithKline.
También podría interesarle


COVID-19 Research Spotlight: Kara Nelson sobre el seguimiento de la propagación a través de las aguas residuales

COVID-19 Research Spotlight: Markita Landry sobre pruebas rápidas basadas en nanosensores

